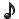VQ: Vector Quantization
چندی سازی برداریVQ: Vector Quantization
چندی سازی برداریپیاده سازی الگوریتم ژنتیک در چندی سازی در متلب
الگوریتم ژنتیک در چندی سازی که توسط نرم افزار متلب پیاده سازی شده است را توضیح می دهیم و سپس برنامه را با مقادیر مختلف اجرا کرده و نتایج را در یک جدول گردآوری گردیده شده است.
الگوریتم را در چند فاز پیاده سازی می کنیمفاز یک: مقداردهی اولیه (Initialize)
در ابتدا باید تعداد جمعیت اولیه(nPop)، بیشترین تعداد تکرار(maxiter)، اندازه بلوک (bs)و کتاب کد(cbs) را مشخص کنیم بنابراین این مقادیر را به عنوان ورودی برنامه دریافت می کنیم
X=inputdlg({'Population','Iteration','Block Size','Codebook Size'}, 'Input', [1 15;1 15;1 15;1 15]);
nPop=str2double(X{1});
nPop=str2double(X{1}); % Number of Fireflies (Swarm Size)
)
maxiter=str2double(X{2}); % Maximum Number of Iterations
bs=str2double(X{3}); % Block Size
cbs=str2double(X{4}); % Codebook Size
و آرایه data را به صورت زیر تعریف می کنیم که دارای دو ستون باشد که دارای لیبلهای Best Fitness و PSNR می باشد.
data={'Best Fitness','PSNR'}; %Row cell array (for column labels)
حال عکس مورد نظر را می خوانیم و آن را خاکستری می کنیم
A = imread('Baboon.jpg'); % Read training image
A = rgb2gray(A); % convert into gray
در واقع عکس به صورت یک آرایه در A ذخیره شده است بنابراین تعداد ردیف ها را با دستور زیر در متغییر h و تعداد ستون ها در w ذخیره می کنیم
[h,w] = size(A);
سپس تعداد بلوک ها را مشخص می کنیم
nb=(h/bs)*(w/bs);
فاز دوم : مقداردهی پارامترها(Parameters setting)
در این مرحله چندین پارامتر را به شرح زیر مقداردهی می کنیم
pc=0.9; % Crossover percentage 0≤ pc ≤1
مقدار نرمال pc برابر با 1 می باشد که مشخص می کند درصد فرزندانی را که از طریق ترکیب تولید می شوند. Pc یک عدد دلخواه می باشد که برای مشخص کردن تعداد کروموزمهایی که عملیات ترکیب روی آنها اعمال می گردد استفاده می شود البته این عدد اختیاری و می تواند مقادیر دیگری را نیز شامل شود. به دلیل آنکه این تعداد باید زوج باشند و تعداد آنها از جمعیت اولیه بیشتر نباشد تعداد جمعیت اولیه را نصف کرده و سپس آن را گرد می کنیم و در دو ضرب می کنیم تا حتما عدد زوج باشد.
ncross=round(nPop*pc/2) *2; % Number of Offsprings(Parents)
pm=0.2; % Mutation percentage 0 ≤ pm ≤ 1
نرخ تاثیر جهش
pm یک مقدار حتمی می باشد که به کمک آن تعداد کروموزوم هایی را که باید جهش داشته باشند را مشخص می کنیم pm را در تعداد جمعیت کل ضرب می کنیم و سپس آن را گرد می کنیم اگر pm=1 باشد بدین معنی است که همه مولفه ها را به صورت تصادفی تعویض کن و اگر pm=0باشد یعنی جهش را انجام نگیرد.
nmut=round(nPop*pm); % Number of mutance
e = .01;
dpr = 10000;
فاز سوم : الگوریتم مقداردهی اولیه جمعیت
نوع تمام مقادیر آرایه A را به نوع double تغییر می دهیم
I=double(A);
با دستور زیر بلوک بندی انجام می دهیم و هر بلوک را در یک ستون قرار می دهیم و در آرایه pool می گذاریم
pool=im2col(I,[bs bs],'distinct');
تعداد سطرهای آرایه pool را در متغییر m و تعداد ستون های آن را در متغییر n قرار می دهد
[m,n]=size(pool);
حال یک ساختار با نام emp با دو متغییر var و fit تعریف می کنیم متغییر fit را با مقدار بینهایت مقداردهی اولیه می کنیم
emp.var=[];
emp.fit=inf;
به منظور ساخت جمعیت باید تابع emp به تعداد جمعیت در یک ستون تکرار گردد
pop=repmat(emp,nPop,1);
حال باید pop را مقداردهی کنیم و بدین منظور حلقه for را به تعداد جمعیت تکرار می کنیم و در هر تکرار چیدمان رندم از n ایجاد می کنیم و سپس تمام سطرهای آرایه pool را از ستون اول تا ستون cbs را متغییر var قرار می دهیم سپس آن را توسط تابع Fitness ارزیابی می کنیم و مقدار آن را در متغییر fit می گذاریم
for i=1:nPop
order=randperm(n);
pop(i).var=pool(:,order(1:cbs));
pop(i).fit =Fitness(pool,pop(i).var);
end
حال جمعیت ایجاد شده را مرتب می کنیم
% Sort Population
pop=SortPopulation(pop);
بهترین عضو را که اولین عضو می باشد را در متغییر BestSol قرار می دهیم
% Store Best Solution
BestSol=pop(1);
حال یک آرایه تعریف می کنیم BsetSol هر بار تکرار را در خود نگهداری کند
% Vector to Hold Best fit Values
BEST=zeros(maxiter,1);
کد زیر حلقه اصلی الگوریتم ژنتیک می باشد که در آن ترکیب ، جهش ، merge ، مرتب سازی ، حذف اعضای اضافه و مجددا این اعمال تکرار می شوند
%% main loop algorithm
It=1;
while It<(maxiter+1)
% crossover
به منظور ساخت جمعیت ترکیب شده باید تابع emp به تعداد ncross در یک ستون تکرار گردد
crosspop=repmat(emp,ncross,1);
سپس این آرایه را به همراه آرایه جمعیت، pool ، تعداد کتاب کد و تعداد کروموزوم هایی که عملیات ترکیب روی آنها انجام می شود را به تابع crossover ارسال می کنیم
crosspop=crossover(crosspop,pop,pool,cbs,ncross);
% mutation
به منظور ساخت جمعیت جهت جهش باید تابع emp به تعداد nmut در یک ستون تکرار گردد
mutpop=repmat(emp,nmut,1);
سپس این آرایه را به همراه آرایه جمعیت، pool ، تعداد کتاب کد و تعداد کروموزوم هایی که عملیات جهش روی آنها انجام می شود را به تابع mutation ارسال می کنیم
mutpop=mutation(mutpop,pop,pool,cbs,nmut,nPop);
% Merge Population
حال جمعیت اصلی را با جمعیت ایجاد شده در عملیات های ترکیب و جهش را به عنوان جمعیت جدید اعمال می کنیم
pop=[pop
crosspop
mutpop];
%roulette wheel
دستورات زیر احتمال هر کروموزوم و سپس جمع احتمال ها از اول تا هر کروموزوم را محاسبه می کنند
f=[pop.fit];
f=max(f)-f+eps;
f=f./sum(f);
f=cumsum(f);
حال در حلقه زیر یک عدد به صورت رندم بین 0 تا 1 انتخاب می شود و اولین f را که شرط زیر برقرار می گردد را انتخاب کرده و سپس عنصر آن را جایگزین می کند
for i=1:nPop
i1=find(rand<=f,1,'first');
pop(i)=pop(i1);
end
% Sort Population
جمعیت pop را به تابع SortPopulation پاس داده تا آن را مرتب نماید
pop=SortPopulation(pop);
% Update Best Solution
در نهایت بهترین کروموزم که اولین آن می باشد را انتخاب کرده و در BestSol قرار می دهد
BestSol=pop(1);
if It == maxiter
break;
else
It=It+1;
end
end
تابع Fitness
این تابع دو آرایه pool و pop(i).var دریافت کرده و در متغیرهای x و y قرار می دهد و سپس تعداد سطرهای تابع pool را در متغییر M و تعداد ستون های آن را در متغییر N قرار می دهد سپس این دو آرایه را به تابع disteu ارسال کرده و این تابع فاصله اقلیدوسی بین آنها را محاسبه کرده و در متغییر d قرار می دهد
function F = Fitness( x,y )
[M, N] = size(x);
d = disteu(x, y);
سپس هر عنصر را به توان 2 رسانده
تابع disteu
این تابع در واقع فاصله اقلیدسی را محاسبه می کند
function d = disteu(x, y)
% DISTEU Pairwise Euclidean distances between columns of two matrices
%
% Input:
% x, y: Two matrices whose each column is an a vector data.
%
% Output:
% d: Element d(i,j) will be the Euclidean distance between two
% column vectors X(:,i) and Y(:,j)
%
% Note:
% The Euclidean distance D between two vectors X and Y is:
% D = sum((x-y).^2).^0.5
[M, N] = size(x);
[M2, P] = size(y);
if (M ~= M2)
error('Matrix dimensions do not match.')
end
d = zeros(N, P);
if (N < P)
copies = zeros(1,P);
for n = 1:N
d(n,:) = sum((x(:, n+copies) - y) .^2, 1);
end
else
copies = zeros(1,N);
for p = 1:P
d(:,p) = sum((x - y(:, p+copies)) .^2, 1);
end
end
end
تابع SortPopulation
این تابع عملیات مرتب سازی کروموزوم ها را انجام می دهد
function [pop Costs]=SortPopulation(pop)
Costs=[pop.fit];
[Costs SortOrder]=sort(Costs,'descend');
pop=pop(SortOrder);
end
عملیات رمزگذاری و رمز گشایی با استفاده از کتاب کد تولید شده را انجام می دهند
%% VQ Encoding
I=double(A);
pool=im2col(I,[bs bs],'distinct');
[m,n]=size(I);
index=zeros(m/bs,n/bs);
for i = 1:numel(index)
temp=repmat(pool(:,i),1,cbs);
[val,ind]=min(sum((temp-BestSol.var).^2));
index(i)=ind;
end
%% VQ Decoding
pool=BestSol.var(:,index(:));
B=uint8(col2im(pool,[bs bs],[h,w],'distinct'));
|
جمعیت |
تکرار |
بلوک |
کتاب کد |
BestSol.fit |
PSNR |
شماره عکس |
|
300 |
20 |
4 |
30 |
e-095.621566281711677 |
20.253630383798340 |
1 |
|
700 |
20 |
4 |
30 |
e-096.824565851631752 |
20.677691126446046 |
2 |
|
1500 |
20 |
4 |
30 |
e-096.135099079110868 |
20.485027793347335 |
3 |
|
5000 |
20 |
4 |
30 |
e-098.499121958083770 |
21.223360355318760 |
4 |
|
10000 |
20 |
4 |
30 |
e-097.471352062573485 |
20.968938692219155 |
5 |
|
300 |
40 |
4 |
30 |
e-092.660062663269436 |
19.274208665165270 |
6 |
|
300 |
60 |
4 |
30 |
e-093.640534994617034 |
19.657035261529730 |
7 |
|
300 |
80 |
4 |
30 |
e-092.590034568803999 |
19.227299420723376 |
8 |
|
700 |
40 |
4 |
30 |
e-094.112299117605227 |
19.712780392131940 |
9 |
|
700 |
60 |
4 |
30 |
e-093.496280994963774 |
19.443884613396545 |
10 |
|
700 |
80 |
4 |
30 |
e-094.716882058054114 |
19.919135288740660 |
11 |
|
1500 |
40 |
4 |
30 |
e-095.123564758476154 |
19.973204641932764 |
12 |
|
1500 |
60 |
4 |
30 |
e-095.303262018582781 |
20.328925380529345 |
13 |
|
1500 |
80 |
4 |
30 |
e-093.720157552976171 |
19.738250231810788 |
14 |
|
10000 |
40 |
4 |
30 |
e-096.324404055253341 |
20.630365676986580 |
15 |
|
10000 |
60 |
4 |
30 |
e-095.073431341348113 |
20.202805235905256 |
16 |
|
10000 |
80 |
4 |
30 |
e-094.169634121448476 |
19.802478345782010 |
17 |
|
300 |
20 |
16 |
30 |
e-111.095891849736290 |
18.254831715897530 |
18 |
|
700 |
20 |
16 |
30 |
e-111.040308130731348 |
18.138778552887200 |
19 |
|
1500 |
20 |
16 |
30 |
e-111.072794272258685 |
18.222451840595410 |
20 |
|
10000 |
20 |
16 |
30 |
e-111.125354901186219 |
18.305255723302132 |
21 |
|
300 |
20 |
4 |
40 |
e-096.781422905094772 |
20.725927258249676 |
22 |
|
700 |
20 |
4 |
40 |
e-097.427667661211070 |
21.034394700434460 |
23 |
|
1500 |
20 |
4 |
40 |
e-097.504545788416165 |
21.114540888457700 |
24 |
|
10000 |
20 |
4 |
40 |
e-097.986502067665150 |
21.060572310664128 |
25 |
|
300 |
20 |
4 |
50 |
e-098.496846154057512 |
21.263864074377356 |
26 |
|
700 |
20 |
4 |
50 |
e-098.712610133475753 |
21.382107685804957 |
27 |
|
1500 |
20 |
4 |
50 |
e-098.835327383145902 |
21.295408225168010 |
28 |
|
10000 |
20 |
4 |
50 |
e-099.020574423322650 |
21.390521871818542 |
29 |
|
300 |
20 |
4 |
60 |
e-098.254206637035775 |
21.415095022060235 |
30 |
|
700 |
20 |
4 |
60 |
e-098.552412545082786 |
21.445611641150606 |
31 |
|
1500 |
20 |
4 |
60 |
e-099.691901907410127 |
21.432221436811872 |
32 |
|
10000 |
20 |
4 |
60 |
e-099.852979368178293 |
21.597368879815980 |
33 |
|
300 |
20 |
4 |
70 |
e-099.606900274959095 |
21.449030823072505 |
34 |
|
700 |
20 |
4 |
70 |
e-099.931360597160332 |
21.580905305218970 |
35 |
|
1500 |
20 |
4 |
70 |
e-099.771556714628313 |
21.533666446488640 |
36 |
|
10000 |
20 |
4 |
70 |
e-081.025573935042055 |
21.710240037195483 |
37 |
|
300 |
20 |
4 |
100 |
e 1.011481866415225 |
21.792009294914347 |
38 |
|
700 |
20 |
4 |
100 |
e-081.113187414833491 |
21.867822159879612 |
39 |
|
1500 |
20 |
4 |
100 |
e-081.035333672534274 |
21.827532770079130 |
40 |
|
10000 |
20 |
4 |
100 |
e-081.176478654361470 |
22.017939492092140 |
41 |
|
300 |
20 |
4 |
500 |
e-081.871144283760800 |
23.246684368486726 |
42 |
|
700 |
20 |
4 |
500 |
e-081.915993552350869 |
23.272559820210603 |
43 |
|
1500 |
20 |
4 |
500 |
e-081.925908365806838 |
23.301261622120750 |
44 |
|
10000 |
20 |
4 |
500 |
e-081.954368329911922 |
23.295674831249430 |
45 |

شکل 1

شکل 2

شکل 3

شکل 4
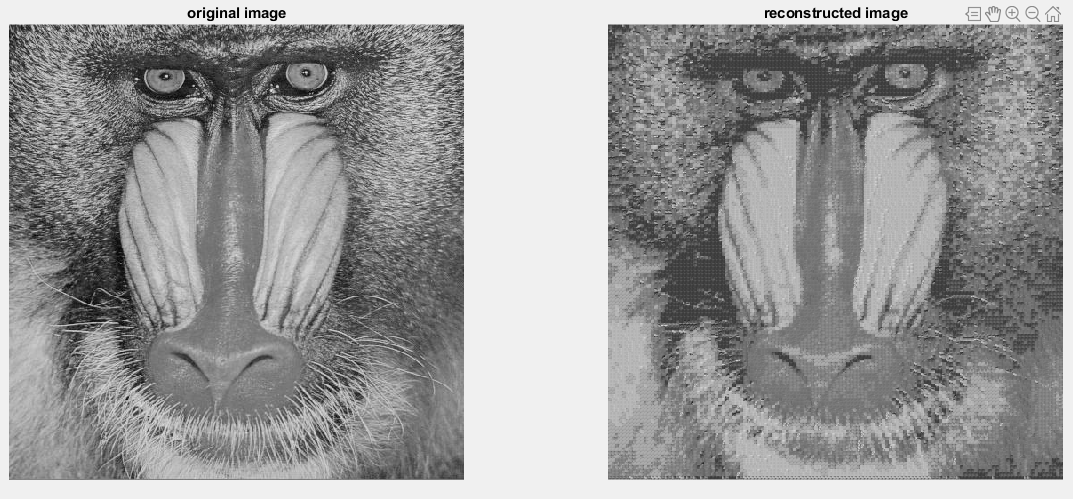
شکل 5

شکل 6
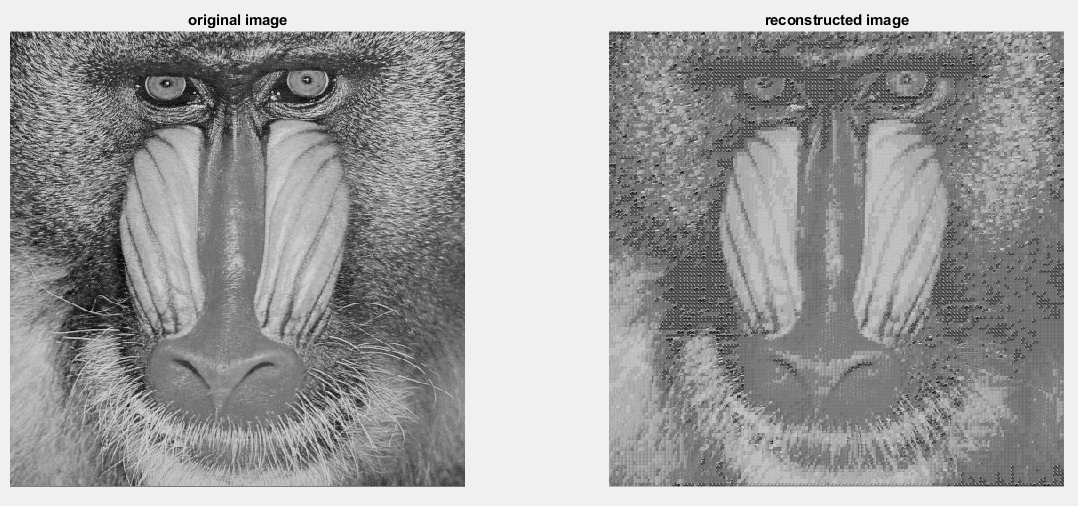
شکل 7

شکل 8

شکل 9

شکل 10

شکل 11

شکل 12

شکل 13

شکل 14

شکل 15

شکل 16

شکل 17

شکل 18

شکل 19

شکل 20

شکل 21

شکل 22
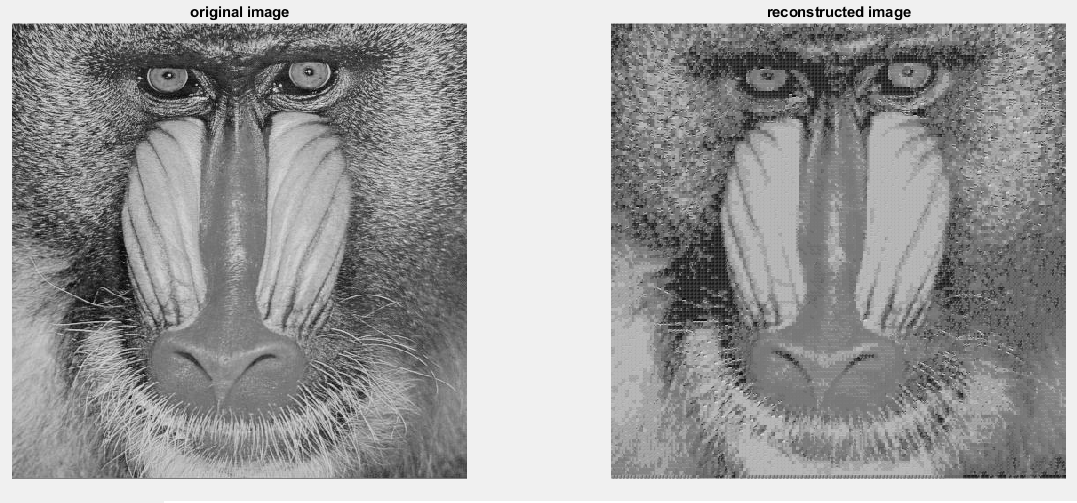
شکل 23

شکل 24

شکل 25

شکل 26

شکل 27

شکل 28

شکل 29

شکل 30

شکل 31

شکل 32

شکل 33

شکل 34

شکل 35

شکل 36

شکل 37

شکل 38

شکل 39

شکل 40

شکل 41

شکل 42

شکل 43

شکل 44

شکل 45